Javier Corral, investigador de la U765 CIBERER en el Instituto Murciano de Investigación Biosanitaria que lidera Vicente Vicente, ha coordinado una investigación en la que ha analizado por primera vez todas las alteraciones genéticas que afectan al codón iniciador de la traducción: 11.261 mutaciones que afectan a 7.205 genes y una media de 12 variaciones de este tipo en cada persona.
Este estudio, publicado en la prestigiosa revista Bioinformatics, está inspirado en una investigación realizada en un paciente con deficiencia de antitrombina, una enfermedad rara que incrementa el riesgo trombótico. La mutación encontrada afectaba al codón iniciador y provocaba la generación de moléculas más pequeñas de este anticoagulante.
La traducción es un proceso biológico clave controlado en las células eucariotas por los codones de iniciación. Variaciones que afectan a estos codones pueden tener consecuencias patológicas que distorsionan la correcta iniciación de esta traducción. Hasta el momento, no había un estudio sistemático que describiera estas variaciones en el genoma humano. Por esta razón, el objetivo del estudio liderado por el Dr. Corral ha sido el desarrollo de herramientas para predecir in silico qué variaciones genéticas que afectan a los codones de iniciación son patogénicas, ya que hasta el momento estos defectos genéticos han sido clasificados erróneamente como missense. La realidad es que cuando se producen estas alteraciones, el ribosoma busca un codón iniciador alternativo, lo que lleva a generar formas más pequeñas o incluso nuevas proteínas.
Esta investigación sugiere diferentes aproximaciones para predecir el efecto de estas alteraciones. La comparación entre las alteraciones con alta y baja frecuencia en la población general ha permitido definir que la distancia del codón alternativo, la conservación del marco de lectura y del péptido señal son parámetros que permiten predecir la patogenicidad de estas mutaciones de forma más acertada que los actuales modelos de predicción.
En la investigación, han colaborado investigadores de la U765 CIBERER y del Departamento de Informática y Sistemas de la Universidad de Murcia.
Abad F, de la Morena-Barrio ME, Fernández-Breis JT, Corral J. "Lost in Translation: Bioinformatic Analysis of Variations Affecting the Translation Initiation Codon in the Human Genome". Bioinformatics. 2018 Jun 1. doi: 10.1093/bioinformatics/bty453.
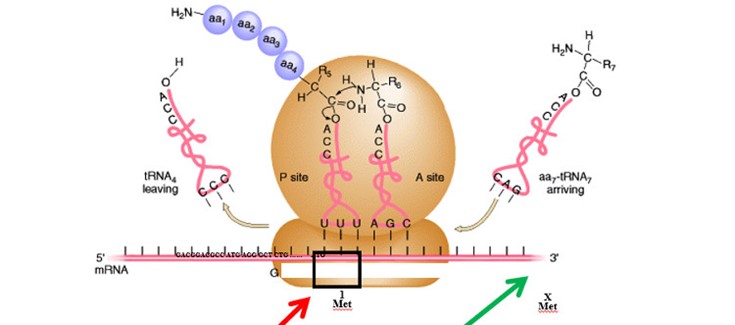
(*) Imagen del inicio de traducción en eucariotas. El ribosoma escanea el RNAm buscando un codón iniciador ATG. Cualquier mutación en el ATG iniciador (o en la secuencia Kozak) provoca que el ribosoma continúe hasta el siguiente codón iniciador, generando una proteína más pequeña o distinta, o incluso no ser productivo.